이전 포스트에서의 내용을 간단히 정리하자면,
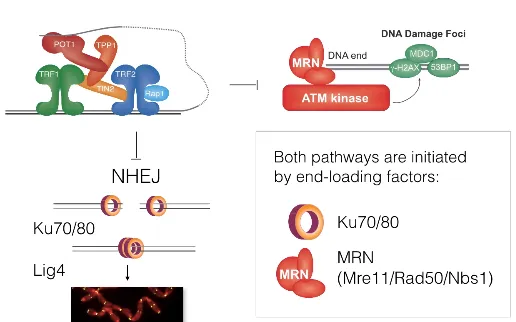
TRF2는 위 그림과 같이 NHEJ, ATM pathway를 block함. 이 때 흥미롭게도 NHEJ의 Ku70/80과 ATM pathway의 MRN이 둘 다 end-loading factor의 일종임. 이 사실이 구체적으로 TRF2가 이들을 block하는 mechanism과 관련되어 있음.
이 mechanism에 대해 본격적으로 알아보기 이전에 우선 telomere 자체가 가지는 non-linear한 structure에 대해 알아보자.

telomere는 위 그림과 같이 t-loop 구조를 이루고 있음. 실제로 위 그림 오른쪽과 같이 단백질이 없는 상태에서 telomere의 t-loop 구조가 EM을 통해 관찰되기도 함.

t-loop는 실제로 위와 같이 형성됨. 보면 ssDNA part인 3' overhang이 dsDNA 내에 invasion되면서 국소적인 D loop를 형성하게 되고, 그 결과 telomere 전체가 t-loop 형상을 띄게 됨. 이는 아마도 ssDNA의 3' part가 DNA repair의 target이 될 수 있기 때문에 dsDNA 사이로의 invasion을 통해 3' part를 protection하기 위해 형성되는 구조일 것으로 생각됨. (다만 system에 따라 3' overhang이 invasion되는 위치가 달라서 t-loop의 크기는 천차만별임)

그런데 이 과정에 TRF2가 관여함.

보면 TRF2, 그 중에서도 TRFH domain이 telomere의 DNA를 감기게 만들고, 그 결과 topological한 변화가 유발되어 보다 쉽게 3' overhang이 invasion되는 것이 가능해짐.

따라서 결국 TRF2는 위 그림에 나타나 있는 것처럼 t-loop를 형성시켜서 노출된 end가 없도록 만들고, 그 결과 NHEJ, ATM pathway가 일어나는것을 block함.
그렇다면 이 사실을 어떻게 입증하였을까. 사실 입증 실험의 idea는 간단함. TRF2가 있을 때, 없을 때 각각에서 t-loop가 만들어지는지 여부를 확인해보면 됨. 그러나 EM 기술은 quantitative analysis에 적합하지 않다 보니 EM만으로는 이 실험을 수행하지 못함.

그 대신 위와 같은 super-resolution STORM imaging 기법이 사용 가능함.

이 기법을 사용해 위 그림과 같이 TRF2가 있을 때, 없을 때 각각에 대해서 t-loop가 생기는지 여부를 확인함. (이 때 TRF2가 없을 때는 일반적으로 telomere간 fusion이 생겨버리므로 제대로 된 image를 얻을 수 없다는 문제점을 해결하기 위해서 ATM null cell을 제작함. 즉, telomere fusion이 일어나지 않도록 조작함) 그 결과 TRF2가 있을 때만 t-loop가 만들어짐을 확인함. 한편 이와는 별개로 TRF1, POT1과 같은 단백질들을 deletion한 채 동일한 실험을 수행했을 때는 t-loop이 잘 형성됨을 확인함. 이를 통해 TRF2가 t-loop 형성에 직접적으로 연관되어있다는 것을 알 수 있음.

결국 TRF2가 없을 경우 t-loop 없이 telomere가 linear하게 남아있게 되고, 그러면 3' overhang을 인지한 Ku70/80에 의해서 NHEJ가 일어나게 되는 것임.

마찬가지로 TRF2가 없을 경우 t-loop가 형성되지 않아 linear하게 남아있게 되는 3' overhang을 MRN이 인지하게 되면 결국 ATM pathway가 일어나게 됨.
그렇다면 Shelterin이 ATR kinase pathway를 block하는 기전은 무엇일까. 결론적으로 Shelterin 중 POT1이 ATR kinase pathway를 block함.

위 실험 결과를 보면 POT1이 있을 때는 telomere가 있는 부위에 53BP1이 recruit되어있지 않지만(붉은색) POT1이 없을 때는 telomere가 있는 부위에 53BP1이 recruit됨. 그런데 53BP1은 ATR pathway에 의해서도, ATM pathway에 의해서도 recruit될 수 있으므로 구체적으로 본 실험에서 둘 중 어떤 pathway에 의해 recruit되는지를 알아야 함.

이를 위해 위 그림과 같이 POT1과 함께 ATR을 제거해줌. 그 결과 53BP1이 recruit되지 않음. 이를 통해 POT1이 ATR pathway를 block하는 녀석이라는 것을 알 수 있음.
그렇다면 구체적으로 어떤 mechanism에 의해 block하는 것일까. 이 mechanism에는 RPA가 밀접하게 관련되어 있음.

보면 실제로 POT1을 없앤 경우 RPA가 telomere 부위에 결합한다는 것을 확인 가능함.
따라서 결국 POT1이 ss telomeric DNA에 결합하면 ssDNA가 cover되는 꼴이므로 RPA가 binding하지 못할 것이고 그 결과 ATR pathway가 활성화되지 못함. 그런데 이 때 문제가 하나 있음. 바로 RPA가 세포 내에 POT1보다 거의 200배 더 abundant하다는 것임. 그리고 RPA와 POT1의 ssDNA binding affinity도 동일함. 그렇다면 도대체 어떻게 POT1이 RPA의 binding을 경쟁적으로 block할 수 있을까. 결론부터 말하자면 POT1이 TRF1, 2에 의해서 Shelterin에 고정되어 있으므로 POT1이 ssDNA에서 잠시 떨어진다 하더라도 이 녀석은 여전히 ssDNA 주변에 머물게 되고, 결국 다시 binding할 수 있게 됨. 반면 RPA의 경우 free하므로 ssDNA에 binding되었다가 다시 떨어지게 되면 결국 diffusion을 통해 멀리 떠나버리게 됨. 그렇기에 POT1이 RPA의 ssDNA binding을 block할 수 있는 것임.

실제로 POT1이 Shelterin의 각종 단백질들에 의해서 tethering되는 것이 정말로 RPA의 ssDNA binding을 block하는지 확인하기 위해 위와 같이 다양한 종류의 돌연변이를 만들고 표현형을 관찰할 수 있음. 보면 POT1 KO, TPP1 KO, TIN2 KO, TIN2 KO+TIN2 mut(이 경우 다시 넣어준 mutant TIN2는 나머지 기능은 모두 정상적이지만 단지 POT1을 recruit하는 활성만 없음) 모두에 대해 ATR active하다는 것이 확인됨. 특히 마지막 결과를 통해서 POT1의 tethering이 RPA의 ssDNA binding block에 중요하다는 것을 알 수 있음.

telomere에는 위 그림과 같이 많은 수의 Shelterin이 결합해 있음. 그런데 이 때 t-loop이 형성되어 있지 않던 형성되어 있던 결국 구조상으로는 ATR pathway가 유발될 수 있는 ssDNA가 항상 존재함. 그러므로 결국 ATR pathway를 block하기 위해서는 POT1이 정상적으로 Shelterin에 tethering되어있어야 함.

지금까지의 내용을 합쳐서 정리한 것이 위와 같음.
이 때 추가적으로 기억해두면 좋은 사항 몇 가지만 짚고 넘어가자. 일단 3' overhang의 경우 telomerase의 합성 방식에 의해 무조건 G-rich할 수 밖에 없음. (C-rich한 3' overhang은 존재하지 않음) 따라서 ssDNA를 인지하는 POT1의 경우에는 특별히 G-rich sequence에 잘 binding되는 특성을 가지고 있어야 할 것임. 실제로 POT1이 G strand에 특별히 잘 binding함을 보여주는 실험 결과가 위 그림 오른쪽 맨 아래에 나타나 있음. (구체적으로는 gel mobility shift assay를 수행함. 참고로 본 실험에서는 antibody까지 동원하지는 않았지만 shift를 일으킨 단백질이 POT1이라는 확신을 얻기 위해서는 antibody를 사용해서 super-shift가 일어나는지를 확인하는 방법을 사용할 수도 있음)
그 밖에 Shelterin과 같은 telomere binding protein들은 telomere length가 너무 길지도, 너무 짧지도 않게 조절해주기도 함.
참고로 telomerase를 사용하지 않고도 telomere를 늘리는 여러 종류의 암세포들이 발견되었고, 이들에 대한 연구를 진행한 결과 Alternative Lengthening of Telomeres(ALT)라는 기작이 제안됨.
다음 포스트부터는 DNA damage와 이를 수선하는 기작들에 대해 알아보도록 하자.
'전공자를 위한 생물학 > 분자생물학' 카테고리의 다른 글
| [분자생물학] 21.2 : BER, MMR, NER, DSB - 1 (0) | 2024.11.01 |
|---|---|
| [분자생물학] 21.1 : DNA damage와 수선 기작 (0) | 2024.10.29 |
| [분자생물학] 20.3 : 텔로미어와 텔로머레이스 - 1 (0) | 2024.10.28 |
| [분자생물학] 20.2 : DNA 복제 종결 (0) | 2024.10.27 |
| [분자생물학] 20.1 : DNA 복제 개시 - 2 (0) | 2024.10.27 |